“一万年不久”—祝贵兵研究组在厌氧氨氧化菌的复苏方面取得进展
“一万年太久,只争朝夕”,一万年对于人类社会非常久远,而对于微生物则不然。
厌氧氨氧化细菌栖息在缺氧的海洋中,它们对全球氮循环有重要贡献。目前已探明,海洋系统中厌氧氨氧化反应对氮的流失贡献量占30-50%,但是在陆地生态系统中厌氧氨氧化反应是否也发挥重要作用,尚不明确。祝贵兵研究员团队此前的研究已经表明,在我国陆地水生态系统中,发生着长期被忽略却又无处不在的厌氧氨氧化过程。但在陆地其他生态系统中,包括森林、草地和荒漠等均没有检测到广泛分布的厌氧氨氧化过程。课题组在北澧河农田生态系统的研究中发现,垂向的旱地土壤,在含水率较高的深度可以检测到厌氧氨氧化反应的发生。因此,我们推测陆地生态系统也广泛存在厌氧氨氧化菌,而水是诱导厌氧氨氧化发生的关键因素。该成果发表于《Environmental Microbiology》。
水是地球生命所必需的,也是微生物能量和代谢的重要介质。休眠是在不利环境下维持低代谢活性的状态。许多微生物在缺水之后会转变为代谢不活跃状态,一旦环境条件变得有利就会恢复。中国科学院生态环境研究中心祝贵兵研究员团队从干旱环境(0-63米)中选择了非常古老的土壤,不加任何其他底物,只在加水培养的条件下,恢复了旱地生态系统中休眠了一万年以上的厌氧氨氧化细菌的活性。同位素示踪分析表明,水诱导硝酸盐还原,生成足够的亚硝酸盐作为底物用于激活厌氧氨氧化菌的能量。随后,硝酸盐异化还原过程 (DNRA)为厌氧氨氧化菌提供了底物铵。从而生成的铵和亚硝酸盐可以反应生成氮气。高通量测序和网络分析表明,Brocadia是厌氧氨氧化菌的优势菌种。Jettenia种属连接其他群落菌群。
这项研究工作的重要意义在于,只用加水的培养方法,成功复苏了休眠了长达一万年以上的旱地土壤中的厌氧氨氧化菌。由此推测,在全球气候变化的影响下,降水增加,土壤水分增加可复活干旱土壤中休眠的厌氧氨氧化菌,从而影响全球氮和碳循环。该成果发表于国际微生物生态学的权威杂志《The ISME Journal》。
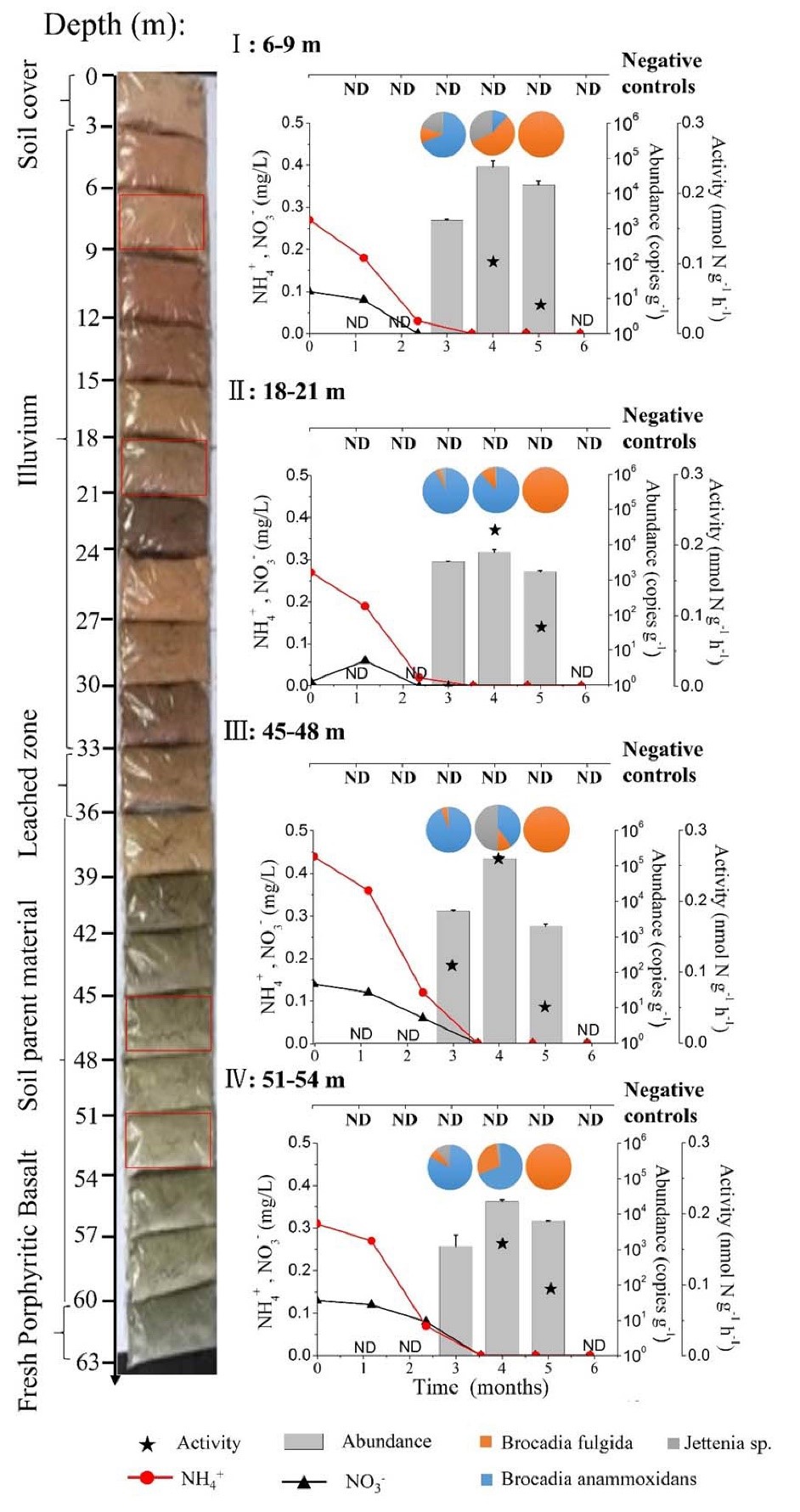
图1 在土壤和风化层深度6-9米(I),18-21米(II),45-48米(III),51-54米(IV),水诱导的Anammox细菌丰度(灰色柱),活性(星状图例),群落组成(饼图)和基质浓度(黑色或红色线),左侧为土壤/风化层演替。“ND”表示厌氧氨氧化物丰度低于检测限(<103拷贝g-1),并且对于厌氧氨氧化速率没有正15N同位素示踪。 数据点代表一式三份实验(平均值±SD)
a.
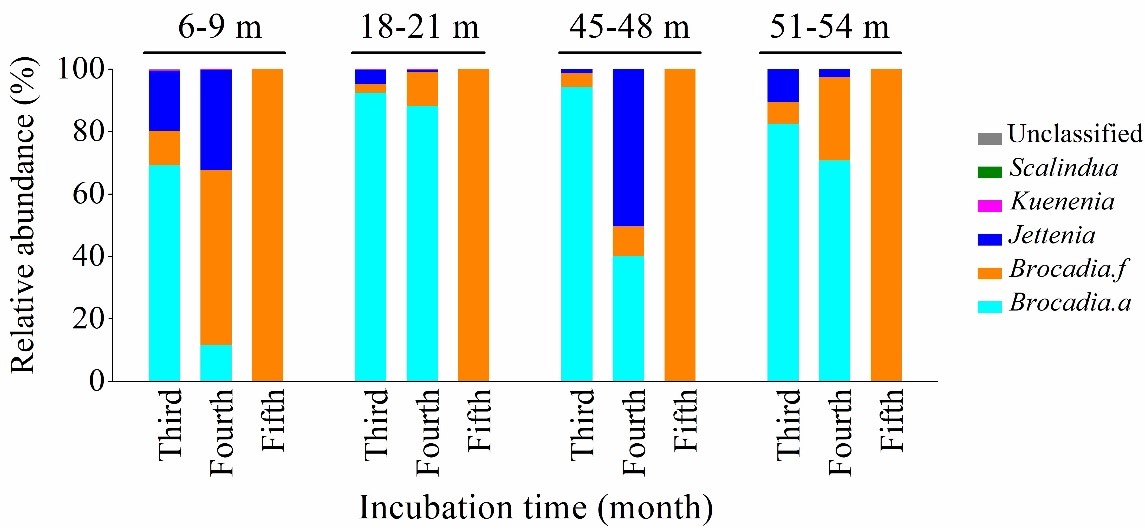
b.
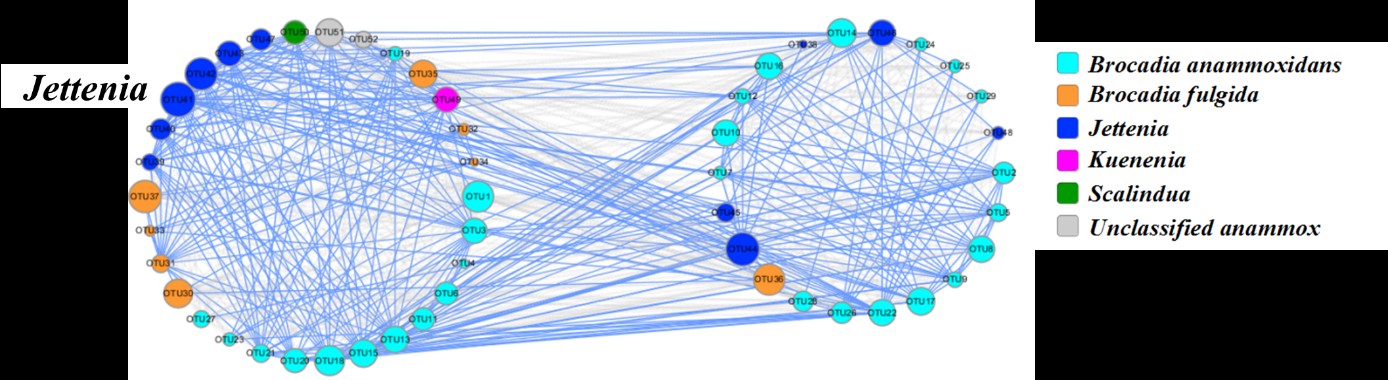
图2 厌氧氨氧化菌细菌群落和内部相关机制概述。a在土壤和风化层深度为6-9米(I),18-21米(II),45-48米(III),51-54米(IV)厌氧氨氧化检测到后的群落组成。b anammox细菌群网络分析图,平均聚类系数(avgCC)为0.639。节点的颜色和形状用于系统发育类群,其大小与节点连通性成比例。蓝色表示正相互作用,灰色表示负相互作用。
a.
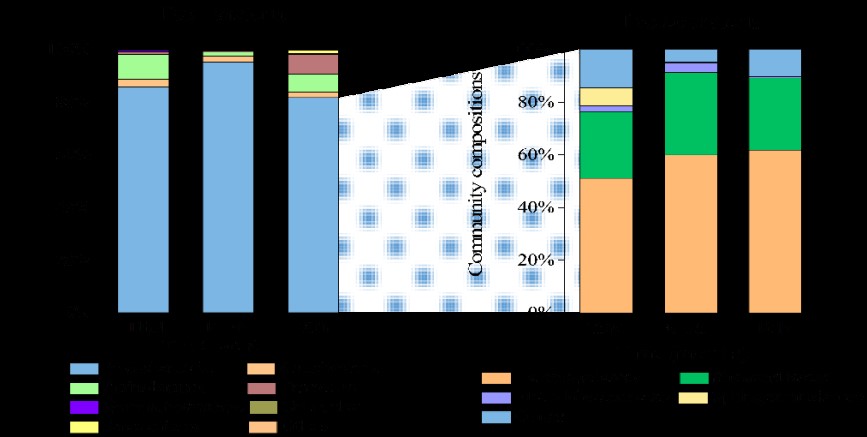
b.
c.
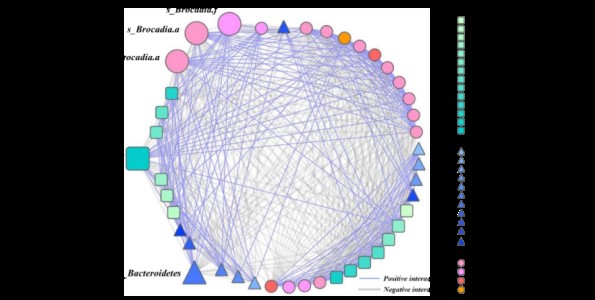
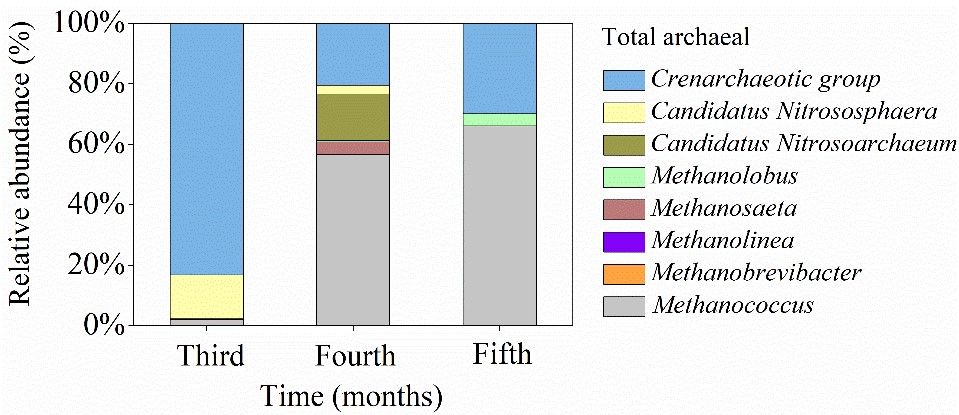
图3 细菌和古菌群落的概述以及与厌氧氨氧化细菌的相关机制。厌氧氨氧化后样品中a 总细菌和丰度最大的门Proteobacteria和b 总古生菌组成的月变化。c土壤/风化土样品在孵化期间厌氧氨氧化细菌,古菌和细菌类群的外相关网络,平均聚类系数(avgCC)为0.704。节点的颜色和形状用于系统发育类群,其大小与节点连通性成比例。 蓝色表示正相互作用,灰色表示负相互作用。

图4 灭菌培养基水培养下土壤/风化土样品中N循环微生物活性和群落的时间变化。
文章列表:
1. Guibing Zhu*, Shanyun Wang, Cheng Wang, Liguang Zhou, Siyan Zhao, Yixiao Li, Fangbai Li, Mike S. M. Jetten, Yonglong Lu, Lorenz Schwark*. Resuscitation of anammox bacteria after >10,000 years of dormancy. The ISME Journal. https://doi.org/10.1038/s41396-018-0316-5
2. Guibing Zhu*, Shanyun Wang, Yixiao Li, Linjie Zhuang, Siyan Zhao, Cheng Wang, Marcel M.M. Kuypers, Mike S.M. Jetten, Yongguan Zhu*. Microbial pathways for nitrogen loss in an upland soil. Environmental Microbiology. 2018. 20(5): 1723-1738.